Metod avslöjar hur proteiner läser RNA‑meddelanden
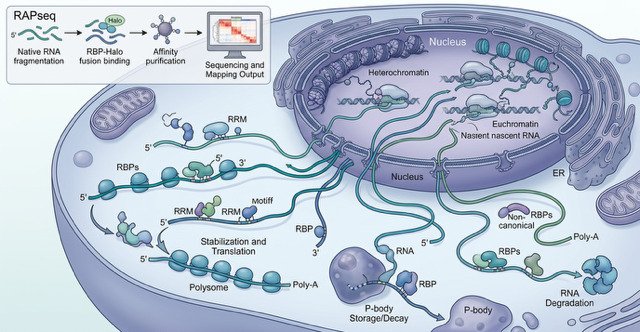
Forskare vid Karolinska Institutet har utvecklat en ny teknik som visar hur proteiner interagerar med RNA-molekylen som bär genetiska instruktioner i våra celler. Studien, som publicerats i Nucleic Acids Research, ger ny kunskap om en viktig del av genregleringen och kan leda till bättre förståelse av sjukdomsmekanismer.
RNA-bindande proteiner (RBP:er) bestämmer när RNA‑meddelanden används, hur länge de finns kvar och hur mycket protein som tillverkas från dem. Men det har länge varit tekniskt svårt att kartlägga dessa interaktioner. I den nya studien presenterar forskargruppen RAPseq, en metod som systematiskt kan visa hur RBP:er binder till RNA i hela transkriptomet.
Med hjälp av RAPseq visade forskarna att både välstuderade och mer okända RBP:er binder till RNA i specifika mönster. De visade också hur cancerrelaterade mutationer förändrar dessa interaktioner, samt identifierade skillnader i RNA‑igenkänning mellan olika ryggradsdjur.

− RAPseq gör det möjligt att fånga hur RNA‑bindande proteiner hanterar genetiska meddelanden, vilket hjälper oss att förstå vad som händer när dessa regleringsprocesser förändras vid sjukdomar, säger forskargruppsledare Claudia Kutter vid institutionen för mikrobiologi, tumör- och cellbiologi vid Karolinska Institutet.
Bidrar till bättre förståelse av sjukdomsmekanismer
Metoden kan användas för att studera tidigare okarakteriserade proteiner, undersöka sjukdomsassocierade varianter och identifiera störda RNA‑nätverk vid till exempel cancer. Den kan också stötta utvecklingen av framtida strategier för att påverka skadliga RNA‑protein‑interaktioner.
− Genom att göra det lättare att studera dessa reglerande händelser hoppas vi att resultaten ska bidra till bättre förståelse av sjukdomsmekanismer och till förbättrade sätt att diagnostisera och behandla sjukdomar, säger Claudia Kutter.
Forskargruppen planerar nu att använda RAPseq på fler mutationer och kombinera metoden med funktionella cellförsök för att identifiera de mest biologiskt relevanta RNA‑protein‑interaktionerna.
Arbetet leddes av forskargruppsledare Claudia Kutter vid Institutionen för mikrobiologi, tumör- och cellbiologi, tillsammans med försteförfattarna Riccardo Mosca, Carlos Gallardo Dodd och Qun Li. Studien stöttades av Knut och Alice Wallenbergs stiftelse, Cancerfonden och Vetenskapsrådet. Se studien för eventuella rapporterade intressekonflikter.
Publikation
"RAPseq enables large-scale identification of RBP-RNA interactions and reveals essentials of post-transcriptional gene regulation", Mosca R, Gallardo-Dodd CJ, Li Q, Sommerauer C, Šidiškis J, Søndergaard JN, Kutter C. Nucleic Acids Research, online 27 februari 2026, doi: 10.1093/nar/gkag090.
